Forscher der Universität Marburg und des “LOEWE”-Zentrums für synthetische Mikrobiologie haben ein molekulares Werkzeug entwickelt, das es ihnen erlaubt, die Stabilität einzelner Proteine in einer Zelle mit Licht zu steuern. Darüber berichten die Wissenschaftler in einem Artikel, der in der nächsten Ausgabe der renommierten Fachzeitschrift “Chemistry & Biology” erscheint.
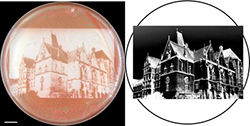 Ein Foto der Alten Universität in Marburg, mit Hilfe des Ein Foto der Alten Universität in Marburg, mit Hilfe despsd-Moduls in beeindruckend hoher Auflösung auf einem Rasen von Hefezellen reproduziert. (Quelle: Chemistry & Biology, Renicke & al., Abb. 3) |
Die Manipulation zellulärer Vorgänge durch Licht bestimmter Wellenlängen hat sich in den vergangenen Jahren zu einer biotechnologischen Trenddisziplin entwickelt, doch bislang wurden in dieser als “Optogenetik” bezeichneten Fachrichtung vor allem Techniken zur Kontrolle der Proteinbiosynthese entwickelt. Der gegenteilige Prozess, der lichtgesteuerte Abbau von Proteinen, ist zwar im Pflanzen- und Tierreich gut bekannt, zum Beispiel bei der Bestimmung von Blühzeitpunkten oder der Regulation der Tag-Nacht-Rhythmik, hat aber noch nicht Einzug in die Biotechnologie gehalten.
Der nun von den Marburger Wissenschaftlern um Dr. Christof Taxis und Professor Dr. Lars-Oliver Essen verfolgte Ansatz ist weitaus vielseitiger und einfacher als der natürliche: Hier wird das ausgesuchte Protein mit einem besonderen Marker verknüpft, um es für den Abbau in der als Proteasom bezeichneten zelleigenen Abbaumaschinerie zu markieren. Das Konstrukt besteht aus einem Lichtsensor der Ackerschmalwand (Arabidopsis thaliana) und einer von den Wissenschaftlern entworfenen Sequenz, die den Abbau durch das Proteasom herbeiführt. Koppelt man dieses sogenannte psd-Modul (für photosensitive degron) an ein Zielprotein und setzt die Zelle blauem Licht aus, verändert der Lichtsensor seine dreidimensionale Struktur und macht die Erkennungssequenz so für das Proteasom zugänglich. Dies induziert den Abbau des Konstruktes samt Zielprotein.
Da der Abbau über das Proteasom in allen höheren Lebewesen gleich abläuft, sollte das neue Modul auch in Pflanzen und Wirbeltieren einsetzbar sein; die Funktionsweise des photosensitiven Degrons haben die Forscher eindrücklich in Experimenten mit der Bäckerhefe (Saccharomyces cerevisiae) gezeigt. So ist es ihnen etwa gelungen, ein Foto der Alten Universität in Marburg auf einem Rasen von Hefezellen zu reproduzieren. Dazu koppelten sie ihr psd-Modul an ein Protein, dessen Abbau zu einer Anreicherung von rotem Farbstoff in den Zellen führt. Über diese Zellschicht legten sie dann ein Schwarz-Weiss-Negativ des Fotos und beleuchteten sie mit blauem Licht –infolgedessen entwickelte sich ein rötlich-beiges Abbild der Alten Universität in beeindruckend hoher Auflösung auf dem Hefe-Rasen. In einem anderen Versuch fusionierten die Forscher ihr Konstrukt mit einem Protein, das für das Wachstum von Hefezellen essenziell ist. In der Kulturschale wuchsen die Zellen daraufhin nur im Schatten einer sternförmigen Maske, der sie vor dem blauen Licht – und damit vor dem Licht-induzierten Abbau des Wachstumsfaktors – schützte.
Kontakt
Dr. Christof Taxis,
Fachgebiet Genetik
Tel: (+49)6421 28-23046
E-Mail: taxis@biologie.uni-marburg.de
Professor Dr. Lars-Oliver Essen
“LOEWE”-Zentrum für synthetische Mikrobiologie
Unit for Structural Biology
Biomedical Research Center / Fachbereich 15 – Chemie
Tel: (+49)6421 28-22032
E-Mail: essen@chemie.uni-marburg.de
Source
Universität Marburg, Pressemitteilung, 2013-04-19.
Supplier
LOEWE-Zentrum für synthetische Mikrobiologie
Philipps-Universität Marburg
Share
Renewable Carbon News – Daily Newsletter
Subscribe to our daily email newsletter – the world's leading newsletter on renewable materials and chemicals









